Riesenviren
von Mario Rembold (Laborjournal-Ausgabe 12, 2013)
Dumm gelaufen für Ralf Hoffmann und seine Koautoren, denn 1998 lag eine kleine Sensation wortwörtlich direkt vor ihren Augen. Schon im Lichtmikroskop erkannten sie die blinden Passagiere in Acanthamoeba, die es sich im Zellplasma bequem gemacht hatten (Endocytobiosis & Cell Res 1998, 12:185-8). Dass sie keinen Vertreter aus den Reihen bekannter Mikroorganismen vor sich hatten, war den Forschern klar. Mit ihrer Vermutung, einen entfernten Verwandten der Archaeen entdeckt zu haben, lagen sie jedoch daneben.
Erst 15 Jahre später sollte das französisch-schwedische Team um die Marseiller Mikrobiologin Chantal Abergel der wahren Natur dieser Zellparasiten auf die Schliche kommen (Science 2013, 341(6143):281-6). Sie züchteten die Parasiten in sterilen Amöbenkulturen und schauten ihnen bei der Vermehrung zu. Ganz offensichtlich reproduzierten sich die Partikel im Zytoplasma, doch die Forscher sahen keine Objekte, die sich teilten. Stattdessen entließen die seltsamen Partikel ihren Inhalt in die Zelle und lösten sich auf, um später wieder in größerer Anzahl zusammengebaut zu werden. Ihr Genom lässt Gene vermissen, die für wichtige Komponenten basaler Zellfunktionen kodieren. Die Parasiten sind nicht mal in der Lage, Ribosomen zu bilden. Und so zeigten die Autoren, was Hoffmann und seinen Kollegen 1998 entgangen war: Offenbar handelte es sich bei den lichtmikroskopisch sichtbaren Strukturen um riesige Viren.
Falsche Bakterien
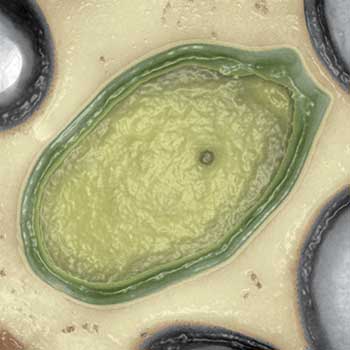
Dem ist fairerweise hinzuzufügen, dass Abergel und ihre Mitstreiter nicht zufällig auf diese Amöbenbewohner gestoßen sind, sondern sich ganz gezielt auf die Suche nach besonders großen Viren gemacht hatten. Ihre Fundstücke tauften sie Pandoraviren. Zwei verschiedene Spezies waren in den Proben enthalten: Pandoravirus salinus aus einer Flussmündung in Chile und Pandoravirus dulcis aus einem Süßwasserteich in Australien. Doch warum ahnte Abergels Team, dass sie in Amöben fündig werden würden? Ganz einfach: Bereits 2003 wurden überdurchschnittlich große Viren in Acanthamoeba identifiziert, ebenfalls in Marseille, jedoch unter der Leitung von Didier Raoult (Science 2003, 299(5615):2033). Dieses „Mimivirus“ war ebenfalls schon zuvor gesichtet worden, man hatte es jedoch fälschlicherweise als Gram-positives Bakterium klassifiziert.
Im Nachhinein wundert es nicht, dass man anschließend vergeblich nach ribosomaler 16S-DNA gesucht hatte, denn die braucht ein Virus nicht. Doch in den 90er Jahren hatte offenbar niemand damit gerechnet, Viren zu entdecken, die sogar im Lichtmikroskop auffallen würden. Historisch galten Viren als Partikel, die einen 0,2-µm-Filter passieren konnten, also entsprechend klein sein mussten. Das 2003 beschriebene Mimivirus hingegen hat eine Länge von 0,4 µm, so dass man damals fast zwangsläufig an Bakterien dachte. Daher auch der Name „Mimivirus“, denn er steht für mimicking microbe.
Während einige Bakterien, wie etwa Mycoplasma genitalium, nur knapp 600 Kilobasenpaare mit sich herumtragen, bringt es Mimivirus auf 800 Kilobasen doppelsträngiger DNA und verfügt über 900 Open Reading Frames. Eine weitere Besonderheit, die 2003 von keinem anderen Virus bekannt war: Mimiviren verfügen über vier eigene Aminosäure-tRNA-Ligasen, wie sie eigentlich, so dachte man, nur in echten Zellen vorkommen. Denn diese Enzyme werden für die Translation gebraucht, damit eine tRNA mit der richtigen Aminosäure verknüpft werden kann.
Virale Rekorde
2011 tauchte dann Megavirus chilensis mit mehr als 1,2 Megabasenpaaren und knapp 1.200 Genen als neuer Rekordhalter auf (PNAS 2011, 108(42):17486-91). Doch die kürzlich entdeckten Pandoraviren setzen noch einen obendrauf. Sie besitzen ein doppelt so großes Genom wie M. chilensis und enthalten potenzielle Gene für mehr als 2.500 Proteine. Mit 1 µm Länge sind sie größer als einige Bakterien. Während Megavirus aber große Übereinstimmung mit Mimivirus zeigt, tanzen die Pandoraviren vollkommen aus der Reihe: 93 Prozent ihrer Gene lassen sich keinem Homolog zuordnen. Zwar besitzen sie ebenfalls Aminosäure-tRNA-Ligasen, doch ist deren größte Übereinstimmung nicht in den entsprechenden Sequenzen von Mimivirus oder Megavirus zu finden, sondern bei ihrem Wirt, Acanthamoeba. Offenbar handelt es sich bei den Riesenviren also nicht um eine einheitliche phylogenetische Gruppe, vielmehr entstammen die Pandoraviren anscheinend einer ganz anderen Linie. Möglicherweise sind sie evolutionsgeschichtliche Überreste einer vierten Domäne des Lebens und gingen aus Zellen hervor, die nicht viel mit den heute lebenden Bakterien, Archaeen und Eukaryoten zu tun hatten.
Zwischen Virus und Zelle
Wo in der Grauzone zwischen unbelebter Materie und einem echten Mikroorganismus steht eine Struktur, die äußerlich nicht von einem Bakterium zu unterscheiden ist und mehr proteinkodierende Sequenzen in sich trägt, als manch ein anerkannter Vertreter der „echten“ Lebewesen? Mehr noch: eine andere Gruppe von Viren nutzt sogar die Maschinerie von Mimivirus für ihre eigene Replikation. Diese Virophagen vermehren sich nur in Zellen, die auch von Mimivirus geentert wurden. Ein Virus also, das von einem anderen Virus ausgebeutet wird. Grotesk. Raoult schlug eine Definition vor, nach der sich eine Zelle durch das Vorhandensein eines Genoms auszeichnet, das Ribosomen kodiert (Intervirology 2010, 53(5):251-3). Ein Virus wiederum müsse neben Nukleinsäuren auch ein Capsid besitzen. Die Natur schert sich nicht um solche Definitionen und Abgrenzungen. Die Frage ist auch, ob man für Viren überhaupt ein phylogenetisches Ordnungssystem aufstellen kann.
Auch wenn die Büchse der Pandora nun geöffnet ist: einige Geheimnisse wird sie wohl für sich behalten.
Letzte Änderungen: 05.12.2013